PCR-DGGE���о�Sludge bio-membrane(SB)ϵͳ��
�����������ı仯
���ͣ����帻���ܿ�Ⱥ����ѩ�ã�����Ƽ���½���
(����ũҵ����ѧԺ ������ѧ�빤��ϵ���㶫 ���ݣ�510225)
ժҪ������SBͬ���ѵ�����ϵͳ��������������������ƽ����뷨��PCR-DGGE����������������Ⱥ�ĸ��١��о����������ͨ��ƽ�巨���뵽��������ҪΪ��״�˾����������˾������ٵ������������˾��ơ�Ī���Ͼ�������������������������7�֣�������ϸ����ҪΪ�����˾������ٵ������������˾��ơ��������4�֣�������ϵͳ��ϸ��������٣������Sequencing Batch Reactor(SBR)�ظ����ķ�����������ͬ������PCR-DGGE�����ָ���ǰ�ԻƸ˾���������˾����������������ɫ�˾�������ϸ����Ϊ�����������Բ���˾����������������ɫ�˾���Ϊ�������������Ψһͨ��2�ְ취���ȷ�ϵķ����������ꡣ����PCR-DGGE��16S rDNA��¡�Ŀⷽ���о���ͬ���������������Ա�����ռ���ơ�
�ؼ��ʣ�������������ϸ����PCR-DGGE����SBϵͳ
��ͼ����ţ�X172 ���ױ�־�룺A ���±�ţ�1672-7207(2011)04-1167-08
Change of denitrifying phosphate bacteria(DPB) in
sludge bio-membrane system using PCR-DGGE method
LIU Hui, SUN Yan-fu, ZHOU Kang-qun, GU Xue-ting, LIU Jie-ping, CHEN Jie-mei
(Department of Environmental Science and Engineering,
Zhongkai University of Agricultural and Engineering, Guangzhou 510225, China)
Abstract: Sludge bio-membrane nitrogen and phosphorus removal system was used to enrich denitrifying phosphorus bacteria(DPB). Plate separation and PCR-DGGE technology were applied to monitor the diversity of bacteria. The results show that before the enrichment, isolated micro-organisms are mainly seven kinds of bacteria including Corynebacterium sp., Acinetobacter sp., Pseudomonas sp., Enterobacteriaceae sp., Moraxella sp., Staphylococcus sp. and Paracoccus sp., seven kinds of bacteria are isolated by the plate separation. After enrichment four kinds of main bacteria i.e., Acinetobacter sp., Pseudomonas sp., Enterobacteriaceae sp., and Paracoccus sp., are found. The species of bacteria are reduced after enrichment and DPB in SB system are different in the SBR. Using PCR-DGGE to investigate bacteria, Flavobacterium sp., Alcaligenes sp., Paracoccus sp., Janthinobacterium sp. and Erythrobacter sp. are mainly five kinds of bacteria before enrichment, but only three kinds of bacteria i.e., Alcaligenes sp., Paracoccus sp., and Janthinobacterium sp. are remained after enrichment. Paracoccus sp. is the only DPB which is confirmed by two methods. Proteobacteria sp. dominates the denitrifying phosphorus bacteria when PCR-DGGE and 16S rDNA clone method are used to analyze the diversity of bacteria.
Key words: denitrifying phosphate bacteria (DPB); bacteria; PCR-DGGE; sludge bio-membrane system
���Ʋ�������ˮ�еĵ�����Ũ���Ƿ�ֹˮ�帻Ӫ��������Ҫ��ʩ����ˣ�����ͬ���ѵ���������Ŀǰ��������ˮ�����о�������ص���ȵ㡣����ˮ��������ʵ�����й����з�����һ�෴��������(��DPB)���������������������л���ͬʱ�ϳ�Ϊϸ���ڴ���Ӫ����PHB(�ۦ�-�ǻ�����)���ͷ��������Σ�����ȱ��������������������Ϊ�������壬���з��������õ�ͬʱ�������ף�ʹ�����ѵ���2�����������ȱ����������ͬһ������һ����ɡ��ɴ˿����Ĺ��ղ����������ѵ���̼Դ����Ҫ�����ҿɽ�ʡ��������������Դ�ͳ��ݣ����⣬ʣ��������Ҳ��� ��[1-3]����һ�ֵ�̼���ܸ�Ч���¼�����Ŀǰ�����ڷ����������о�������SBR��Ӧ����ʵ���Ҳ����˹�ģ���ˮ�����о�[4-6]�����ǣ�������������SB��������������Ĥ����ϵͳ(SBϵͳ)������ʵ�ʵ���ˮ������ͬ�������������о��������١�������Ծ����������з�������������ı仯�о����٣����ܿ�Ⱥ��[4-6]�Է���������SBRϵͳ�е�������ɲ��ô�ͳ�����﷽���������о�������Ϊֹ������PCR-DGGE������SBϵͳ�ڸ���������������Ⱥ�仯��ϵͳ�о���δ�����ױ��������о�����SBϵͳ������������������3�������ε���ˮ���ҺΪ�о���������������Ⱥ�仯�ĸ������о���Ϊ�о�SBϵͳ�е���Ⱥ�����Լ�����������ѧ�����������в�ͬʱ��װ������ȡ��ˮ���Һ������ƽ����뷨��PCR-DGGE��ͬ�����ٲ�ͬѱ�������η�����������Ⱥ�ı仯������Ա�Ϊ�����������ո������ܾ��꼰�����Ľ�һ���о��ṩ�ο���Ϊ��ͳ���ѵ������յĸ������¹��յĿ�����Ӧ���ṩ������
1 �����뷽��
1.1 ���鷴Ӧװ��
�о�����Sludge bio-membrane(SB)ϵͳ����װ�ü�ͼ1����ˮ����Ϊ1 m3/d����������Ԫ�IJ����ֱ�Ϊ��(1) ��������������������ˮ��ͣ��ʱ��(HRT)Ϊ3.3 h��������ԭ��λ(ORP)С��-100 mV��(2) ���ٳ�������HRTΪ0.32 h��(3) ����Ĥ����HRTΪ2.2 h��ORP����+200 mV��(4) ������������HRTΪ0.6 h��ORPС��+50 mV��(5) ȱ���������෴������������ HRTΪ2.7 h��ORPΪ0~-100 mV��(6) ��������HRTΪ0.15 h��(7) ��������HRTΪ0.3 h��
1.2 ���Բ���
1.2.1 ������ˮ
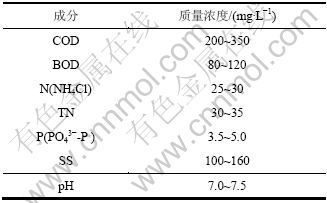
������ˮ���Թ�����ij��ˮ��������ʵ����ˮ,��ˮ���������1��
��1 ������ˮ�ɷ�
Table 1 Composition of sewage wastewater
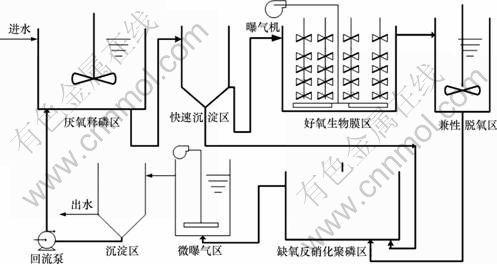
ͼ1 ��������������Ĥ����ϵͳ
Fig.1 Activated sludge and bio-membrane combined system
1.2.2 Sludge bio-membrane(SB)ͬ���ѵ�����ϵͳ�����з���
ȡ������������ˮ������A2/O�����λ������ࡣ���������1�е�������ˮ���(��(MLSS)=3.5~4.0 g/L),������Ĥ����������Ӧ�������������Ϊ�������帻�����������������з�����3���Σ��ȷֶ����к��������С�
��1��ΪĤ�����ص������Ρ�Ŀ���Ƕ�ϵͳ�е����������и����Ӷ�����ˮ�еİ���ת��Ϊ�����ε���Ϊ��2�θ��������������ṩ�����ε��ĵ������塣���������õĹ���������ˮ��A2/O���պ����λ������������ij��ˮ��������ˮ��ϣ�ORP������80~100 mV��������3�¡�
��2��Ϊ�����������ĸ������豸���ԽΡ��ýε�Ŀ���ǣ�(1) ȥ������ķ�������(���з��������ö���������)��(2) ͨ�����������׳غ�ͬ�����������׳ؽ������У����ýӴ������ز�����������Ϊ�������壬�Է�������������ѡ��������ö�����������Ĺؼ�������1�εĺ���Ĥ�������а���ת��Ϊ�����ε���ת�����ȶ���90%���Ϻ��豸�����2�Σ���ͬʱ�������������������ٳ���������������Ĥ����������������ȱ�����������������������Ͷ��γ������������Ϊ������������(3.30 h)�����ٳ�����(0.32 h)����������Ĥ��(2.20 h)������������(0.20 h)��ȱ��������������(2.70 h)��������(0.15 h)�����γ�����(0.34 h)��ʽ���У���ʼ��������Ũ�ȿ�����2.0~2.5 g/L��ȱ��ORPΪ-100~-120 mV������ORPΪ-150~-220 mV��������6�¡�
��3��Ϊ��ϵ���ȶ��Ρ�Ŀ���ǣ�����������������һ������һ��������ϵ���ȶ��ԣ�װ�ù�����40 d��
����3�����е�39 dʱ����ˮTP����Ũ��Ϊ0.65 mg/L(��1.00 mg/L)���ܵ�����Ũ��Ϊ12.6 mg/L(��15.0 mg/L)����������Ũ��Ϊ3.8 mg/L(��5.0 mg/L)��COD����Ũ��Ϊ34 mg/L(��50 mg/L)��������GB18918��2002����Ҫ��ϵͳ��ˮTP���ܵ���������CODŨ�ȱ仯���ȶ���С���ɴ˽�һ��˵����ϵ�����ȶ����С�
��������õ�2�ο�ʼ�͵�3��ĩ�ڷ�����������������(��ʱ������ȥ���ʸߴ�90.26%�������ε�ȥ���ʸߴ�92.31%)Ϊ�о����࣬������봿����Ĵ�������Ϊ�о�����
1.2.3 ��������Һ
��ˮ������5.0 g��KH2PO4 0.025 g��MgSO4?7H2O 0.5 g��CaCl2?H2O 0.2 g��(NH4)2SO4 2.0 g����Ԫ�� 1.0 mL������ˮ1 000 mL��pH=7.0��
1.3 ���鷽��
1.3.1 ������������ķ���
��1.2.2�е��о����������ţ����൰�����������������ϡ�Ͷ�ƽ���ϵ�һ���侭��ƽ�廮�ߴ����õ����꣬�ø��ͻ����ܷ���ء�
1.3.2 ͬ������������������̬�۲졢��������ָ��
�����������и�����Ⱦɫ����100��10����ѧ�����¹۲���ɫ����̬�����в������顢�����λ�ԭ���������λ�ԭ������������Ⱦ����PHBȾɫ����Ҫ��������[7]���顣
1.3.3 DNA��ȡ��PCR�������������бȶԼ�����������
�Ի�õ���������������ռ���������TE����Һ(pH=8.0)ϴ�ӣ�ͨ���ܾ�ø�ѽ�Ͷ��ڲ����ѽ�ϸ������SDS�ͷ�/�ȷ���ȡ������DNA��16S rRNA�����������ùѾۺ���������27 f��1522 r��PCR����������94 ��Ԥ����4 min����94 �����1 min����55 �渴��1 min����72 ������2 min��30��ѭ���������72 ������7 min�������������Ϻ�Ӣ�����\������˾��������16S rDNA�������У���GenBank���ݿ��н���BLAST���е�������� ��[8-9]��ͬʱ���������������16S rDNA���У�����ϵͳ�����������ж�����CLUSTAL X1.83 ���ж�����ƥ�����У��������Ĺ�����Neighbour-joining��������������֦ģʽ���ȶ�����MEGA 4.0����bootstrap�������ظ�1 000�Σ��������֧��֧�ֶȡ�
1.3.4 PCR-DGGE���������
(1) ��ƷDNA���Ʊ��������ĺ��Bead- Beating��[10]����Ʒ�м���20 mL���Ỻ��Һ(0.1 mol/L Tris��Cl��0.1 mol/L EDTA-Na2��0.2 mol/L NaCl��1% PVP��2% CTAB��pH=8.0)������30 min��������15 min������10 mg/mL���ܾ�ø����37 ����45 min������1.5 mL 20%SDS��65 ��ˮԡ1 h�����ĺ��ռ����塣�����÷ӡ��ȷ¡����촼(�����Ϊ25:24:1)����3�Σ���������Ũ��Ϊ0.3 mol/L��NaAc(pH=5.2)��0.6��NaAc��Һ�����������������³���1 h��ת��Ϊ13 000 r/min������20 min���ռ�����������70%�Ҵ�Ưϴ2�Σ����ɺ�����50 ��L TE�С�����0.8%��֬��������Ӿ��⡣
(2) 16S rDNA-V3������������Ʒ�ֱ�ϡ��50�������16SrDNA-V3�������������ΪF357(��GC����)��5��CGCCCGCCGCGCGCGGCGGGCGGGGCG- GGGGCACGGGGGGCCTACGGGAGGCAGCAG3����R518��5��ATTACCGCGGCTCGCTGG 3����25 ��L�ķ�Ӧ��ϵ����H2O 0.25 ��L��10��Buffer(��2.0 mol/L MgCl2)2.0 ��L��dNTP(10 mol/L) 1.0 ��L��F338(10 ��mol/L) 1.0 ��L��R518(10 ��mol/L)1.0 ��L��Taq(5 U/��L) 0.1 ��L��ģ��DNA 1.0 ��L����Ӧ����Ϊ����94 ��Ԥ����4 min����94 �����0.5 min����52 �渴��1 min����72 ������0.5 min��30��ѭ������72 ������7 min����Ӧ�����1.2%��֬��������Ӿ��⡣
(3) DGGE��ʵ����̡�DGGE����BIO-RAD DGGE��Ӿ�ǡ��۱�ϩ��������Ũ��Ϊ8%�������ݶ�Ϊ35%~65%(100%���Լ�����7 mol/L���غ�40%������)����Ӿ����Ϊ��60 �棬180 V����Ӿ5 h��0.04���GoldviewȾҺ30 min������������ϵͳ(GDS-8000)���ࡣ
(4) DNA�Ļ��պ�PCR��������DGGE�н��������õ������м�����������ˮ��4 �����24 h������ģ��ʹ�á�����Ʒ����16SrDNA-V3�������������ΪF338��5��ATTACCGCGGCTCGCTGG 3����R518��5��ATTACCGCGGCTCGCTGG 3����25 ��L�ķ�Ӧ��ϵ����H2O 0.25 ��L��10��Buffer(��2.0 mmol/L MgCl2)2.0 ��L��dNTP(10 mmol/L)1.0 ��L��F338(10 ��mol/L)1.0 ��L��R518(10 ��mol/L)1.0 ��L��Taq(5 U/��L) 0.1 ��L��ģ��DNA 1.0 ��L����Ӧ����Ϊ����94 ��Ԥ����5 min����94 �����30 s����55 �渴��40 s����72 ������40 s��30��ѭ������72 ������7 min���������Ϻ�Ӣ�����﹫˾���С�
2 ���������
2.1 �����������ʹ����Ľ��
�ڵ�2�͵�3�ηֱ�����������17���11�ꡣ���ϸ������Ҫ��������ָ��[7]��16S rDNA��������������2��
�ӱ�2���Կ�������2�ε�ϸ����ҪΪ��״�˾����������˾������ٵ������������˾��ơ�Ī���Ͼ�������������������������7�֣���3�ε�ϸ����ҪΪ���Ϊ�����˾������ٵ������������˾��ơ��������4�֣���������ϵͳ��ϸ�������ڼ��٣����ܿ�Ⱥ��[4-5]��SBR��Ӧ���з��뵽�ķ����������Լٵ�����������״�˾���Ϊ�������˾��ƺ������������֮��������[6]��A2/O-SBR��Ӧ���з��뵽�ļٵ���������Ī���Ͼ��������˾���ϸ���������������Լ������˾��������ﷴ�����ѵ����������������أ�ռȫ�������66.16%�����½�����������ԭ���ǣ��������Sludge bio-membrane (SB)ͬ���ѵ�����ϵͳ����ˮˮ������ˮ��������ʵ����ˮ����ˮ�е�̼Դ�ɷָ��ӣ���������[6]����ʵ��������ˮ�����Դ�����Ϊ��Ҫ̼Դ�����⣬����������ͬ����ˣ���������ϵͳ��������ɺ���������һ���IJ��졣��˵����Ӧ����������Ⱥ��ɺͱ仯��ӳ�������ѵ�������ϵ����״����
��2 SBͬ���ѵ�����ϵͳ��ͬ������Ҫ��ϸ������
Table 2 Main bacteria of SB simultaneously nitrogen and phosphorus removal system during different stages ��

2.2 ����PCR-DGGE����SBϵͳ����Ķ�����
2.2.1 DGGEͼ����
ͼ2�е���Ʒ�ֱ�ȡ�Ե�2�εĿ�ʼ(����������������ǰ������A)�͵�3�ε�ĩ��(����������������������B)����ͼ2��֪������B��DGGEͼ����ijЩλ��������A�ıȽϽӽ�������ijЩλ�ô�����һЩ���졣����ƷA��a��b��c��d��e���������������϶���˵������ǰ���ַḻ����ͬ�������λ�ý�Զ���Һ�����˵������֮��IJ���Ƚ����ԣ������ʾ��װ��������Ķ����ԡ�������ԭ�������ڸ���ǰ����ȡ��A/A/O���������أ�A/A/O����Ϊһ������ϵͳ�����зḻ��������Ⱥ����Ҫ�о��������������ȼ�����������
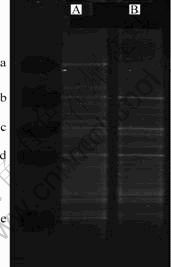
ͼ2 DGGEͼ��
Fig.2 Profile of DGGE
����������������ƷB�е�b��c��d�������ڣ����ҽ��������ǣ�a��e������ʧ����˵������һ��ʱ��ĸ���������ˮ����ռ���Ƶ�������Ⱥ������2�֣�����Ķ����Գ��½����ơ���˵�������ķ�ʽ�����ڷ�����������������
2.2.2 ���������Ļ��ղ���ͽ�������
ѡȡ���д����Ե�����a��b��c��d��e�н�����DNA����Ϊģ�����PCR�������Բ���ֱ�Ӳ���ʹ��GenBank��BLAST������ǰ���5�����������ݿ����ѵ�¼�����н���ͬԴ�ԱȽ�,����Clustal W(Versionl.8)���ж�����ƥ�����У�ѡȡ�������ݿ��е����У���Neighbour-joining������������������������֦ģʽ���ȶ�����MEGA4.0��������bootstrap�������ظ�1 000�Σ��������֧��֧�ֶȣ���ϲ�����ϸ�������ֲ�ͳ���ϸ�������ֲ�[7-10]����������ָ��Ϊ���ݼ���������������£�
(1) a��Flavobacterium sp.(�Ƹ˾���)����Ե��ϵ��ӽ�������ͬԴ��Ϊ95%���Ƹ˾���[11-12]�Ǹ������Ը˾���ֱ��״����Բ�����ȡ�����Ϊ(0.5~0.8) ��m��(1.0~3.0) ��m���Ƿ����ͣ��ں�̼ˮ��������Һ�ڵķ�Ӧһ�㲻����Ҳ��������Ҳ�м��������ͣ�����ʻ�ɫ���ɫ���������л�����Ӫ�����Ӵ�ø������ø������ø��Ϊ���ԣ�ϸ���ڲ����ۦ�-�ǻ������Σ���Щ�����ܻ�ԭ�����κ��������Ρ�ͬʱ����Ϸ�Ӧ����������ȥ���ʸߴ�90.26%����ˣ�a��Flavobacterium sp.(�Ƹ˾���)�����ƣ��Ƿ���������
(2) b��Alcaligenes sp.DQ435021(����˾���)����Ե��ϵ��ӽ���ͨ�����������бȶԣ����е�ͬԴ��Ϊ96%������˾����Ǹ������Ը˾������������ͣ��ܹ����ô�����Ϊ̼Դ��������лΪ�Ƿ������ͣ����к������������ԡ��е��������λ��������δ��ڣ���ͨ�������������з������������κ�����������Ϊ�������壬�Ӷ���������[13]�������ֵ�[13-15]��������������ֳ����õķ���������Ч�����ɴ���Ϊb�����˾���Alcaligenes sp.�����ƣ��Ƿ�����������
(3) c��Paracoccus sp.(�������)�����ƣ����е�ͬԴ��Ϊ94%������������Σ��ʵ������ɶԻ�Ѵ��ڣ�ֱ��Ϊ(0.5~0.9) ��m�����˶����������Ρ��������λ�����������ʱ����������Ϊ������������������������������������½������λ�ԭΪ�������ε���������N2����ˣ�����Ϊ���������ܡ�ͬʱ����ø�ͽӴ�ø��Ӧ�����ԡ�
(4) d��Janthinobacterium sp. (��ɫ�˾���)��Ե��ϵ��Ϊ�ӽ������е�ͬԴ��Ϊ96%����ɫ�˾���������������ɫ������[16-17]������Բ�˵ĸ˾�����������Ϊ���������Ը˾������˶��ԣ���Ĥ������������Ϊ���������������Ƿ����ͣ��Ӵ�ø���ԣ��������ԣ�����ø���ԣ���ԭ�����κ��������Σ���ʱ�������壬���˲����������з��������ܡ�����δ�����Ƿ���з����������ܣ��ɴ��ƶϵó�d��Janthinobacterium sp.(��ɫ�˾���)�����ƣ�ͬʱ��һ�ַ���������
(5) eΪ��ϸ����(Erythrobacter sp.)�����е�ͬԴ��Ϊ97%�������������P������ٻ�ɫ���ɫ����������һ�ֹ��ϸ��,����Ӫ��������ˮ�������[18]���������ֳ�ܼ����ͺ����С���˾����Ǹ��������Ը˾������������������ͣ����Թ��������͡������õ�̼ԴΪ�������Ρ���ͪ���Ρ������Ρ��Ȱ����μ������ǡ�������Ҫά���ء���������¶�Ϊ25~30 �棻pHΪ7.0~8.0����Ҫ1.7%~3.5% NaCl���ܽ������λ�ԭΪ�������Ρ��ɴ��ƶϵó�e��Erythrobacter sp.�����ƣ����з��������ܡ�
����������aӦ������Flavobacterium sp.(�Ƹ˾�������Flavobacteria)��bӦ������Alcaligenes sp.(����˾�����-proteobacteria)��cӦ������Paracoccus sp.(�������������-proteobacteria)��dӦ������Janthinobacterium sp.(��ɫ�˾�����- proteobacteria)��eӦ������Erythrobacter sp.(��ϸ������-proteobacteria)�����У�b��cΪ������������a��eΪ����������d�Ƿ�������������������д���һ���о���
2.2.3 ����ǰ���Ⱥ��ṹ����
����ƷA��a��b��c��d��e�����������ֱ����Ϊ�Ƹ˾���������˾����������������ɫ�˾�������ϸ���������в���˾������������Ϊ��������������ɫ�˾������Ƹ˾�������ϸ����Ϊ������������˵������������������A/A/O���յ��������У�ֻ������A/A/O���յ����з�ʽ����ʹ���Ϊ������Ⱥ��Ҳ�п����Ƿ�����������A/A/O��������������������������ص㡣
Bˮ���еĴ�������Ϊ3�����ֱ�Ϊ�Ƹ˾����������������ɫ�˾�������ͼ2���Կ�����7�־��������������Ϊ4�֣�����ʾSBͬ���ѵ�����ϵͳ����������Ķ����������½���������Ϊͨ���������к��÷����������ո������ṩ������ȱ������Ļ��������ҿ�����ˮ��COD����Ũ�ȡ��������������������ˮ��COD����Ũ�ȣ���ʹȱ���ؽ�ˮCOD������Ũ�ȵ���50 mg/L����������COD�Է�����������Ӱ�죬�����˴ֳ��淴����������������˼�����������רְ�ķ����������Ӷ�ʹ�����з��������ܵij�ϸ��������̭����Ⱥ��������֮����[5]���������������ܵIJ���˾��������������Ȼ���ڣ����˵��ϵͳ�ĸ�����ʽ�����ڷ��������������档����һ�����Ǹ�����d����(��ɫ�˾���)��������Ӧ����������ȥ���ʸߴ�90.26%�������ε�ȥ���ʸߴ�92.31%����ɫ�˾�������������ָ��ȷ����Ϊ�������������Ҵ�ͼ3��ʾ��ϵͳ��������֪����˾����������������ɫ�˾���3�־�������Ե��ϵ�ӽ������Ƹ˸˾����ͳ�ϸ��������Ե��ϵ��Զ����ˣ���ɫ�˾����ľ������д��ڽ�һ��ȷ����
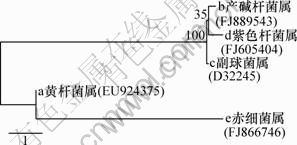
ͼ3 SMϵͳ�����ƾ�Ⱥ��ϵͳ������
Fig.3 Phylogenic tree construction of dominate bacteria in SM system
2.2.4 PCR-DGGE����ƽ�巨�ıȽ�
�ӱ�2���Կ������������ϸ����ҪΪ�����˾������ٵ������������˾��ơ��������4�֡���ͨ��PCR-DGGE�������֪����������Ҫ�ķ���������Ϊ����˾������������2�֣����и������Ϊ2�ַ���ͬʱ��õ�Ψһ������������Ϊ����ƽ����뼼������������һ�������ܵ��������������ƣ��õ��ľ��������ޣ�������DGGE-PCR�����õ��ľ��ֶ������ḻ���������ڸ÷���Ҳ���������ľ�����, ��Щƽ������ľ�����������ʾ, ��ˣ����ߵ��������غ϶Ȳ����ߡ��������ֶ�ϵͳ���������������Ĺ����д��ڽ�һ�������о���
���������Ψһͨ��2�ְ취���ȷ�Ϸ����������ܵľ��ꡣ�ܿ�Ⱥ��[4]���ô�ͳ������SBR��Ӧ���з���ķ���������(DPB)�Լٵ�����������״�˾���Ϊ�������˾��ƺ������������֮������� ��[19]����PCR-DGGE���������DPBΪgamma- Proteobaccteria�Ǹ��е�Chromatiaceae��(������98%)��Ahn��[20]����PCR-DGGE���������DPB��Ҫ�к컷����Rhodocyclus sp.(96%���ƶ�)�� Dechlorimonas sp. (97%ͬԴ��)�����Ƕ������ڱ��ξ���Ȼ����ͨ��FISHֻ�����˺컷������Tsuneda ��[21-22]������/����SBR����������뵽��DPBΪThauera mechernichensis (83%���ƶ�)�̵�������Azoarcus tolulyticus (83%���ƶ�)���䶼���ں컷��������������ǹ������״α����ķ�����������
2.2.5 PCR-DGGE����16S rDNA��¡���ıȽ�
��ʵ���в���DGGE�Ľ������ϸ���У��Ƹ˾���(Flavobacteria�٣�Ϊbacteroidetes��)������˾���(��-proteobacteria��)���������(��-proteobacteria��)����ɫ�˾���(��-proteobacteria��)��Erythrobacter sp.(��ϸ������-proteobacteria)���Ա�����(proteobacteria)Ϊ�������뽹��־��[14, 23]���о����һ�¡�����־��[14]����ƽ����뷨���ּٵ��������Ͳ���������ѵ�����Ч����ã�����DGGE������ϵͳ�з���������������Ⱥ����Ҫ��Ϊ7��Ⱥ, �ֱ���Anaerolineae(��), Actinobacteria(���߾���), Bacteroidetes (��˾���)��TM7����-proteobacteria(���θ�)����-proteobacteria(���θ�)�ͦ�-proteobacteria(���θ�)��Ⱥ�����У�Actinobacteria(���߾���)�ͦ�-proteobacteriaΪ���Ƶķ��������������������з��־������������Ժ����˾����������ƣ�Ҳ����һ����֤���˲���˾���Ϊ������������������ ��[23]����16S rDNA��¡�Ŀⷽ���Ը�Чͬ���ѵ�����ϵͳ��ϸ�������˶������о������������ϵͳ������ϸ����ȺΪProteobacteria��Ⱥ(���ξ���Ⱥ)��ռ 55.17%��ϸ����Ⱥ����˳��Ϊ��-Proteobacteria��Ⱥ(34.48%)��Bacteroidetes��Ⱥ(�Ƹ˾���Ⱥ��20.69%)����-Proteobacteria��Ⱥ(12.07%)��Candidate division TM7��Ⱥ(12.07%)����-Proteobacteria ��Ⱥ(5.17%)����-Proteobacteria��Ⱥ(3.45%)��Firmicutes��Ⱥ(��ھ���Ⱥ��3.45%)��Candidate division OP11��Ⱥ(1.72%)��Planctom ycetes��Ⱥ(��ù״����Ⱥ, 1.72%)����Ϊ��¡������õĻ������зdz��̣���ˣ��ܶ�ϸ�����������������о�ϵͳ�ڵ�����ȫ�浫����ȷ��������PCR-DGGE����õĻ������г��X�٣���ˣ�ϸ����ȷ�����ǣ���Ϊֻ����ijЩ�����Ĺ���ϲ�����ȡ�������У���ˣ���ȫ�淴ӳϵͳ������Ķ����ԣ��ʲ��ò�ͬ���о��������Ӳ�ͬ���о��ǶȲ���ȫ��λ�˽�ϵͳ�ڲ�����Ķ����Ժ� ���ԡ�
���۲���PCR-DGGE�о�SBͬ���ѵ�����ϵͳ��SBR���е����ƾ����Լ�����16S rDNA��¡�Ŀⷽ���о���Чͬ���ѵ�����ϵͳ��ϸ�������Ա�����(proteobacteria)ռ���ơ�
3 ����
(1) ͨ��ƽ�巨���뵽��������ҪΪ��״�˾����������˾������ٵ������������˾��ơ�Ī���Ͼ�������������������������7�֣�������ϸ����ҪΪ�����˾������ٵ������������˾��ơ��������4�֣���������ϵͳ��ϸ��������٣������SBR�ظ����ķ������������ͬ��
(2) ����DGGE��������Ʒ����ǰ�ԻƸ˾���������˾����������������ɫ�˾�������ϸ����5�־�Ϊ�����������Բ���˾����������������ɫ�˾���3����Ϊ�������������Ψһͨ��2�ְ취���ȷ�Ϸ����������ܵľ��꣬��������δ��������
(3) Sludge bio-membrane(SB)ͬ���ѵ�����ϵͳ�в���PCR-DGGE����õľ��������ƾ���ͬ��16S rDNA��¡�Ŀⷽ����õľ����Ϊ�ḻ�����ǣ�proteobacteria��Ϊ�����ѵ�����ϵͳ�ж�ռ���ơ�
�ο����ף�
[1] Meinhold J, Filipe C D M, Daigger G T, et al. Characterization of the denitrifying fraction of phosphate accumulating organisms in brological phosphate removal process[J]. Wat Sci-Tech, 1999, 39(1): 31-42.
[2] Kuba T, van Loosdrencht M C M, Brand F A, et al. Occurrence of denitrifying phosphorus removing bacteria in modified UCTtype wastewater treatment plants[J]. Water Research, 1997, 31(4): 777-786.
[3] Kuba T, van Loosdrecht M C M, Heijnen J. Phosphorus and nitrogen removal with minimal COD requirement by integration of denitrifying dephosphatation and nitrification in a two-sludge system[J]. Water Research, l996, 30(7): l702-l7l0.
[4] �ܿ�Ⱥ, ����, ���帻, ��. ������������SBR ��Ӧ����������Ⱥ��Ũ�ȱ仯[J]. ���ϴ�ѧѧ��: ��Ȼ��ѧ��, 2008, 39(4): 705-711.
ZHOU Kang-qun, LIU Hui, SUN Yan-fu, et al. Change of microorganism amount and species in SBR reactor enriching denitrifying phosphate bacteria[J]. Journal of Central South University: Science and Technology, 2008, 39(4): 705-711.
[5] �ܿ�Ⱥ, ����, ���帻, ��. A2/O�������о����ķ�������������ѧ���Լ���������Ӱ�������о�[J]. ���ϴ�ѧѧ��: ��Ȼ��ѧ��, 2007, 38(4): 645-649.
ZHOU Kang-qun, LIU Hui, SUN Yan-fu, et al. Denitrifying phosphorus accumulation characteristic of PAO from A2/O anaerobic stage and affecting factor of characteristic utilization[J]. Journal of Central South University: Science and Technology, 2007, 38(4): 645-649.
[6] ����, ��Դ, ����Ӣ, ��. ����˫�����ﷴ���������ѵ�ϵͳ����������[J]. �й���ˮ��ˮ, 2003, 29(8): 33-35.
LUO Ning, LUO Gu-yuan, JI Fang-ying, et al. Microbial buildup on new two-sludge system for nitrogen and phosphorus removal[J]. China Water and Wastewater, 2003, 29(8): 33-35.
[7] ������, ����Ӣ. ����ϸ��ϵͳ�����ֲ�[M] . ����: ��ѧ������, 2001: 164-169.
DONG Xiu-zhu, CAI Miao-ying. Manual of ordinary systemic bacteriology[M]. Beijing: Science Press, 2001: 164-169.
[8] ������, ������. �����еķ�������ѧ��ϼ���[M]. ����: ��ѧ��ҵ������, 2004: 132-165.
WANG Ai-jie, REN Nan-qi. Diagnosis technology of molecular biology in the environment[M]. Beijing: Chemical Industry Press, 2004: 132-165.
[9] ���, ����ɽ, ������. ������ˮ��������[M]. ����: ��ѧ��ҵ������, 2003: 360-361.
LI Jun, YANG Xiu-san, PENG Yong-zhen. Microbiology and water treatment engineering[M]. Beijing: Chemical Engineering Press, 2003: 360-361.
[10] Chen B Y, Janes H W. PCR cloning protocols[M]. Totowa: Humana Press, 2002: 33-45.
[11] van Trappen S, Vandecandelaere I, Mergaert J, et al. Flavobacterium degerlachei sp. nov., Flavobacterium frigoris sp. nov. and Flavobacterium micromati sp. nov., novel psychrophilic bacteria isolated from microbialmats in Antarctic lakes[J]. International Journal of Systematic and Evolutionary Microbiology, 2004, 54: 85-92.
[12] van Trappen S, Tan T L, Samyn E, et al. Flavobacterium frigoris sp. Alcaligenes aquatilis sp. nov., a novel bacterium from sediments of the Weser Estuary, Germany, and a salt marsh on Shem Creek in Charleston Harbor, USA[J]. International Journal of Systematic and Evolutionary Microbiology, 2005, 55: 2571-2575.
[13] ������, ������, �, ��. ˫�����ѵ�����ϵͳ�о����������о�[J]. �й���ˮ��ˮ, 2008, 24(7): 4-7.
PAO Lin-lin, LI Xiang-kun, LI Dong, et al. Study on characteristics of phosphorus accumulating organisms in a continuous flow two sludge system for nitrogen and phosphorus removal[J]. China Water and Wastewater, 2008, 24(7): 4-7.
[14] ����־, ������, ������, ��. ��������������ɸ����������Է���[J]. ����������ѧѧ��: ��Ȼ��ѧ��, 2009, 25(3): 535-539.
JIAO Zhong-zhi, LI Xiang-kun, ZHANG Li-cheng, et al. Isolation and characteristic of denitrifying phosphorus accumulating organism[J]. Shenyang Architectural University: Science and Technology, 2009, 25(3): 535-539.
[15] ������, ��ʥ��, ��ˮ��. ��̼ͬԴǿ���������ϵͳ��PCR-DGGE����[J]. ��������ҵ��ѧѧ��, 2007, 39(4): 589-593.
LIU Ya-nan, XIA Sheng-ji, YU Shui-li. Application of polymerase chain reaction-denaturing gradient gel electrophoresis to analyze biological phosphorus removal systems fed with different carbon sources[J]. Journal of Harbin Institute of Technology, 2007, 39(4): 589-593.
[16] Kampfer P, Falsen E, Busse H J. Reclassification of Pseudomonas mephitica Claydon and Hammer 1939 as a later heterotypic synonym of Janthinobacterium lividum (Eisenberg 1891) de Ley et al. 1978[J]. International Journal of Systematic and Evolutionary Microbiology, 2008, 58: 136-138.
[17] �γ�ϼ, ��ӱ. һ�������ϩ������ø����ɫ�˾��ķ��������о�[J]. ��У����ѧ��, 2006, 20(5): 769-774.
SONG Zhao-xia, ZHANG Ying. Optimization of fermentation conditions for a pva-degrading enzyme producing strain[J]. Journal of Chemical Engineering of Chinese Universities, 2006, 20(5): 769-774.
[18] Yoon J H, Oh T K, Park Y H. Erythrobacter seohaensis sp. nov. and Erythrobacter gaetbuli sp. nov., isolated from a tidal flat of the yellow sea in Korea[J]. International Journal of Systematic and Evolutionary Microbiology, 2005, 55: 71-75.
[19] �����, ������, ֣����. ������Ϊ��������ķ���������������[J]. �й�������ѧ, 2008, 28(12): 1094-1099.
JIANG Yi-feng, ZHU Yun-ye, ZHENG Jian-jun. Feasibility of denitrifying phosphorus removal technique using nitrite as electron acceptor[J]. China Environmental Science, 2008, 28(12): 1094-1099.
[20] Ahn J, Daidou T, Tsuneda S, et al. Characterization of denitrifying phosphate-accumulating organisms cultivated under different electron acceptor conditions using polymerase chain reaction-denaturing gradient gel electrophoresis assay[J]. Water Research, 2002, 36: 403-412.
[21] Tsuneda S, Miyauchi R, Ohno T. Characterization of denitrifying polyphosphate-accumulating organisms in activated sludge based on nitrite reductase gene[J]. Journal of Bioscience and Bioengineering, 2005, 99(4): 403-407.
[22] Tsuneda S, Ohno T, Soejima K, et al. Simultaneous nitrogen and phosphorus using denitrifying phosphate-accumulating organisms in a sequencing batch reactor[J]. Biochemical Engineering Journal, 2006, 27: 191-196.
[23] ������, ����Ϫ, ����, ��. 16SrDNA��¡�Ŀⷽ������MDAT2IATͬ���ѵ�����ϵͳϸ���������о�[J]. ������ѧѧ��, 2006, 26(6): 903-911.
WANG Hai-yan, ZHOU Yue-xi, DAI Xin, et al. Bacterial diversity study for the simultaneous nitrogen and phosphorus removal system (MDAT2IAT) by 16S rDNA cloning method[J]. Acta Scientiae Circumstantiae, 2006, 26(6): 903-911.
(�༭ ����ƽ)
�ո����ڣ�2010-02-23�������ڣ�2010-05-12
������Ŀ��������Ȼ��ѧ����������Ŀ(51078008)���㶫��Ȼ��ѧ��ѧ����������Ŀ(06022869��07003251)���㶫ʡ��������Ŀ(LYM08067)�������к������Ƽ��ƻ���Ŀ(2007-Z-023)
ͨ�����ߣ�����(1973-)��Ů�����������ˣ���ʿ�о����������ڣ�������ˮ���ﴦ���ͻ�������ѧ���о����绰��020-89003191��E-mail��gzzkq@126.com